RELECOV 2.0 – Consolidación de las actividades de WGS y RT-PCR para SARS-CoV-2 en España hacia un uso sostenible y la integración de la infraestructura y procesos mejorados en la red RELECOV
Datos
Acrónimo: RELECOV 2.0
Referencia: Project 101113109. EU4H-2022-DGA-MS-IBA-1
Socios – Coordinación: Laboratorio de Referencia de Virus Respiratorios en el Centro Nacional de Microbiología (Instituto de Salud Carlos III, ISCIII)
Duración: Julio de 2023 a marzo de 2026
Presupuesto: 2.200.421,27 €
Objetivo principal: Consolidar una infraestructura nacional de vigilancia genómica basada en secuenciación del genoma completo para el seguimiento del SARS-CoV-2 y otros virus respiratorios.
Ámbito: Red nacional que integra laboratorios hospitalarios, centros de investigación y organismos de salud pública de toda España.
Co-financiación: Programa europeo EU4Health

Resumen del proyecto
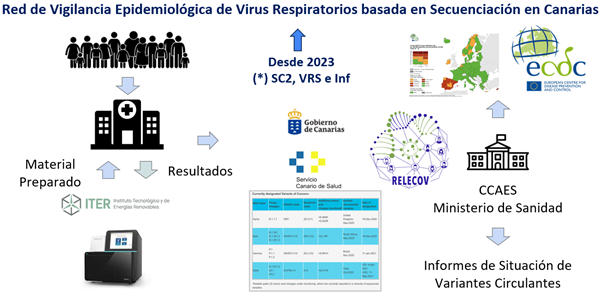
La vigilancia genómica se ha convertido en una herramienta clave para comprender y responder a las enfermedades infecciosas emergentes. En este contexto surge la Red Nacional de Laboratorios para la Secuenciación Genómica del SARS-CoV-2 o RELECOV, al amparo de un proyecto europeo orientado a consolidar en España una infraestructura nacional de vigilancia basada en secuenciación genómica que permita detectar, monitorizar y comprender la evolución de virus respiratorios que causan infección respiratoria aguda.
La RELECOV está coordinada por el Centro Nacional de Microbiología del Instituto de Salud Carlos III, que integra laboratorios de microbiología y centros de investigación de todas las comunidades autónomas.
Objetivos del proyecto.
La RELECOV inició su andadura en el año 2021 a raíz de la pandemia de la COVID-19 con el fin de reforzar la capacidad de secuenciación genómica en España y mejorar la identificación y seguimiento de las variantes del SARS-CoV-2, estableciendo una red coordinada de laboratorios a nivel nacional, siguiendo las recomendaciones de la Organización Mundial de la Salud y la Unión Europea.
El proyecto RELECOV 2.0, que ha sido cofinanciado por el programa europeo EU4Health (2023–2025) y las comunidades autónomas, ha pretendido identificar y consolidar las diferentes capacidades y recursos para integrar la secuenciación del genoma completo de virus de interés para el Sistema Nacional de Salud en la vigilancia epidemiológica. Para ello, se trabaja en la integración de tecnologías de secuenciación del genoma completo y herramientas avanzadas de análisis bioinformático. Así, durante estos años se ha pasado de una red nacional inicial centrada fundamentalmente en la secuenciación del virus SARS-CoV-2 (RELECOV 1.0) a una red ampliada (RELECOV 2.0) en la que se obtiene de forma rutinaria la secuencia del genoma de varios virus que causan infección respiratoria aguda, incorporando el seguimiento del virus de la gripe y del virus respiratorio sincitial (VRS).
Entre los principales objetivos de la RELECOV destacan:
- Identificar y monitorizar variantes de interés y preocupación del SARS-CoV-2, así como nuevos linajes emergentes.
- Ampliar la vigilancia genómica a otros virus respiratorios, como el virus de la gripe o el virus respiratorio sincitial.
- Consolidar una plataforma nacional de análisis y gestión de datos genómicos, que permita compartir información entre laboratorios y con repositorios internacionales.
- Establecer metodologías y protocolos comunes de secuenciación y análisis, facilitando la interoperabilidad entre centros participantes.
Una red colaborativa para la salud pública frente a futuras amenazas sanitarias
Uno de los pilares del proyecto ha sido su enfoque colaborativo. RELECOV conecta laboratorios, centros hospitalarios y centros de investigación de todo el país, lo que permite generar conocimiento de forma coordinada y compartir protocolos, datos y resultados. El Área de Genómica del ITER — auspiciado por el Cabildo Insular de Tenerife — participa desde el primer momento en esta red junto al personal del Servicio de Microbiología del Hospital Universitario Ntra. Sra. de Candelaria (HUNSC) e investigadores del grupo de “Variación Genética y Enfermedad” de la Fundación Canaria Instituto de Investigación Sanitaria de Canarias (FIISC) en el HUNSC, como centro de referencia para la comunidad autónoma (ver Figura 1).
Además, la RELECOV 2.0 busca establecer las bases de una plataforma de vigilancia genómica adaptable a nuevos patógenos emergentes y reemergentes. La integración de tecnologías de secuenciación, análisis bioinformático y compartición de datos está permitiendo detectar cambios en la secuencia genética de los virus de forma rápida para mejorar la preparación frente a futuras epidemias o pandemias, facilitando información útil a las autoridades de salud pública de todo el país.
A lo largo de estos años, el equipo HUNSC-FIISC-ITER ha logrado poner a punto diferentes protocolos para la secuenciación genómica de estos virus respiratorios.
En el caso de la gripe, se ha diseñado un protocolo en abierto que facilita el estudio ágil y eficiente de cepas del virus de la gripe A, permitiendo la caracterización de la secuencia de consenso de diferentes cepas del virus que circulan cada año en la población (como A/H1N1 y A/H3N2) y versiones del virus que causan estragos entre los animales, como la gripe aviar (A/H5N1). En este sentido, cabe destacar que el equipo canario ha participado en todos los ejercicios de intercomparación y evaluación de la calidad de la secuenciación, con resultados exitosos.
Desde la temporada 2023-2024, la RELECOV integra el seguimiento epidemiológico basado en secuenciación del virus respiratorio sincitial. Este virus es la principal causa de infecciones respiratorias graves a nivel mundial en población infantil (especialmente recién nacidos y lactantes) y personas mayores, ocasionando el 80% de las bronquiolitis y neumonías en estos grupos etarios, respectivamente. El VRS es un virus que circula en la población durante todo el año, aunque su acción se hace más notable en otoño e invierno. El grupo de trabajo ha implementado una metodología que permite la preparación rápida y secuenciación de muestras de personas infectadas por VRS, facilitando la obtención rápida de la secuencia genética, con unos resultados muy prometedores (https://github.com/genomicsITER/RSV; https://github.com/genomicsITER/nf-rsvpipeline).
En el marco de esta red, los laboratorios de la RELECOV generan información que es canalizada por el Instituto de Salud Carlos III hacia el Ministerio de Sanidad del Gobierno de España y el Centro Europeo de Control y Prevención de Enfermedades (ECDC). En este sentido, el proyecto representa un paso importante hacia la consolidación de la vigilancia genómica como herramienta estructural de la salud pública, alineada con las estrategias europeas de preparación ante amenazas sanitarias.
La participación del ITER e impacto en Canarias
La participación del ITER en el grupo de trabajo HUNSC-FIISC-ITER de la RELECOV 2.0 constituye un caso de éxito del principio de cooperación entre administraciones, a través de entidades cuyas sinergias representan una clara apuesta de cara a reforzar las capacidades de vigilancia genómica en Canarias, permitiendo aplicar tecnologías avanzadas de secuenciación y análisis bioinformático para el seguimiento de virus que causan infección respiratoria aguda. Esta iniciativa favorece la transferencia de conocimiento entre centros de investigación, servicios de salud y organismos públicos, fortaleciendo la preparación del archipiélago ante posibles brotes o amenazas sanitarias. Asimismo, la participación en redes nacionales y europeas como RELECOV permite integrar los datos generados en Canarias dentro de sistemas de vigilancia epidemiológica más amplios, contribuyendo a una respuesta coordinada frente a los retos de la salud pública.
El ITER participa en RELECOV 2.0 aportando su demostrada experiencia en el análisis bioinformático y procesamiento de datos genómicos masivos. Desde la entidad se contribuye al análisis de las secuencias virales obtenidas mediante tecnologías de secuenciación de segunda y tercera generación, así como al desarrollo y puesta en producción de flujos de trabajo computacionales para el procesamiento y la interpretación de los datos genómicos.
La infraestructura computacional del ITER, TeideHPC, permite gestionar rápidamente los grandes volúmenes de datos generados por la secuenciación de virus respiratorios, facilitando la identificación de variantes, el análisis filogenético y la generación de información útil para la vigilancia epidemiológica.
El proyecto RELECOV ha elaborado un folleto informativo, disponible para su descarga en los siguientes enlaces:
Publicaciones científicas
Gómez-Del Rosario A, Muñoz-Barrera A, Alcoba-Florez J, García-Martínez de Artola D, Rodríguez-García N, Lorenzo-Salazar JM, González-Montelongo R, Flores C, Ciuffreda L. A bench-to-data analysis workflow for respiratory syncytial virus whole-genome sequencing with short and long-read approaches. Genome Med. 2026 Jan 27;18(1):9. doi: https://doi.org/10.1186/s13073-025-01597-4
Repositorios de GitHub